Un gran avance en la investigación del coronavirus da como resultado un nuevo mapa para apoyar el diseño de la vacuna
Anuncios
Investigadores de la Universidad de Texas en Austin y de los Institutos Nacionales de Salud han hecho un avance crítico hacia el desarrollo de una vacuna para el nuevo coronavirus del 2019 al crear el primer mapa a escala atómica en 3D de la parte del virus que se adhiere e infecta a las células humanas.
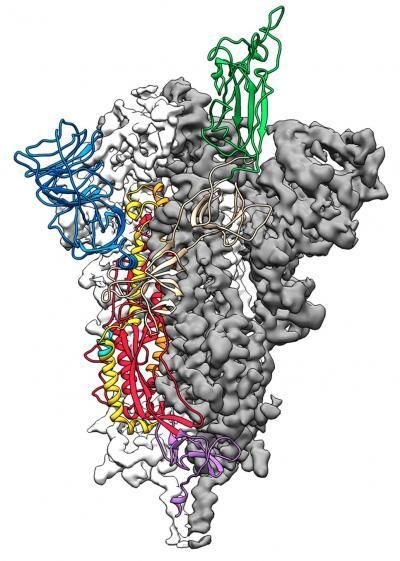
Este es un mapa a escala atómica en 3D, o estructura molecular, de la proteína de punta 2019-nCoV. La proteína toma dos formas diferentes, llamadas conformaciones, una antes de infectar una célula anfitriona y otra durante la infección. Esta estructura representa la proteína antes de que infecte una célula, llamada la conformación de prefusión.
Jason McLellan/Univ. of Texas at Austin
El mapeo de esta parte, llamada la proteína de punta, es un paso esencial para que los investigadores de todo el mundo puedan desarrollar vacunas y medicamentos antivirales para combatir el virus.
El equipo científico también está trabajando en un candidato de vacuna viable relacionado con la investigación.
Jason McLellan, profesor asociado de UT Austin que dirigió la investigación, y sus colegas han pasado muchos años estudiando otros coronavirus, incluyendo el SARS-CoV y el MERS-CoV. Ya habían desarrollado métodos para bloquear las proteínas de los coronavirus en una forma que las hiciera más fáciles de analizar y que pudiera convertirlas efectivamente en candidatas para las vacunas. Esta experiencia les dio una ventaja sobre otros equipos de investigación que estudiaban el nuevo virus.
"Tan pronto como supimos que se trataba de un coronavirus, sentimos que teníamos que saltar a él", dijo McLellan, "porque podríamos ser uno de los primeros en conseguir esta estructura. Sabíamos exactamente qué mutaciones poner en esto, porque ya hemos demostrado que estas mutaciones funcionan para un montón de otros coronavirus".
La mayor parte de la investigación fue realizada por los co-autores del estudio, el estudiante de doctorado Daniel Wrapp y el investigador asociado Nianshuang Wang, ambos en UT Austin.
Apenas dos semanas después de recibir la secuencia del genoma del virus de los investigadores chinos, el equipo había diseñado y producido muestras de su proteína de punta estabilizada. Llevó unos 12 días más reconstruir el mapa 3D a escala atómica, llamado estructura molecular, de la proteína de espiga y presentar un manuscrito a la Ciencia, que aceleró su proceso de revisión por pares. Los muchos pasos que implica este proceso normalmente tardarían meses en llevarse a cabo.
Un factor crítico para el éxito fue la tecnología de punta conocida como microscopía electrónica criogénica (crio-ME) en el nuevo Laboratorio Sauer de Biología Estructural de UT Austin. La crio-EM permite a los investigadores hacer modelos 3D a escala atómica de estructuras celulares, moléculas y virus.
"Terminamos siendo los primeros en parte debido a la infraestructura del Laboratorio Sauer", dijo McLellan. "Destaca la importancia de financiar las instalaciones de investigación básica".
La molécula que el equipo produjo, y para la cual obtuvo una estructura, representa sólo la porción extracelular de la proteína de punta, pero es suficiente para provocar una respuesta inmunológica en las personas, y así servir como una vacuna.
A continuación, el equipo de McLellan planea usar su molécula para seguir otra línea de ataque contra el virus que causa COVID-19, usando la molécula como "sonda" para aislar los anticuerpos producidos naturalmente de los pacientes que han sido infectados con el nuevo coronavirus y se han recuperado con éxito. En cantidades suficientemente grandes, estos anticuerpos podrían ayudar a tratar una infección de coronavirus poco después de la exposición. Por ejemplo, los anticuerpos podrían proteger a los soldados o a los trabajadores de la salud enviados a una zona con altas tasas de infección en un plazo demasiado corto para que la inmunidad de una vacuna surta efecto.
Barney Graham, subdirector del Centro de Investigación de Vacunas (VRC) de los NIH en Bethesda, Maryland, ayudó a supervisar los experimentos y a co-escribir el manuscrito.
Nota: Este artículo ha sido traducido utilizando un sistema informático sin intervención humana. LUMITOS ofrece estas traducciones automáticas para presentar una gama más amplia de noticias de actualidad. Como este artículo ha sido traducido con traducción automática, es posible que contenga errores de vocabulario, sintaxis o gramática. El artículo original en Inglés se puede encontrar aquí.