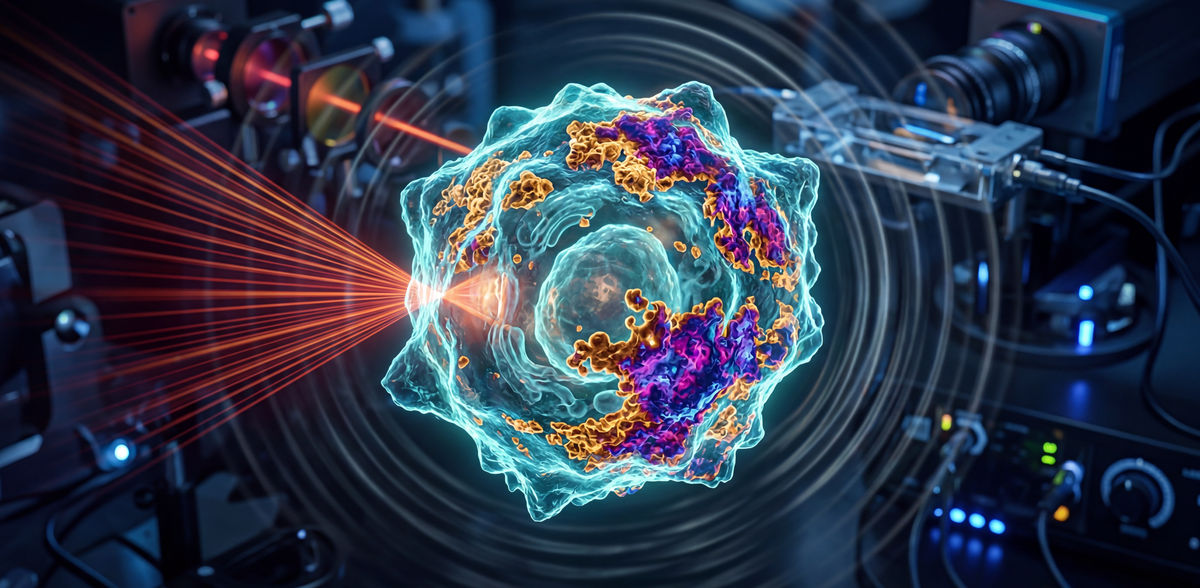
Identification des lipides : une empreinte chimique au lieu d'un colorant
Annonces
Une équipe du Helmholtz Munich et de l'université technique de Munich (TUM) a mis au point une nouvelle technique de microscopie qui permet de distinguer les espèces lipidiques dans les cellules vivantes - en particulier le cholestérol et la sphingomyéline - et de les cartographier sans qu'il soit nécessaire de les étiqueter chimiquement. En combinant l'illumination dans l'infrarouge moyen et la détection optoacoustique, la méthode lit les empreintes spectrales naturelles des lipides, éliminant ainsi le besoin d'étiquettes fluorescentes spécifiques, dont la mise au point est laborieuse et qui peuvent interférer avec la fonction des lipides. L'équipe présente ses résultats dans la revue Nature Methods.
Les lipides sont des éléments clés des membranes cellulaires et contribuent à contrôler la façon dont les cellules transmettent les signaux et transportent les substances. Toutefois, la détection ou la visualisation de classes de lipides spécifiques dans les cellules vivantes est un défi. La microscopie à fluorescence traditionnelle nécessite le développement d'étiquettes fluorescentes personnalisées pour chaque lipide - un processus long et coûteux - et ces étiquettes peuvent parfois affecter la fonction du lipide, stresser les cellules ou ne pas se lier spécifiquement à la cible visée.
La lumière infrarouge moyenne et les ultrasons rendent les lipides visibles sans étiquette
Une équipe dirigée par le professeur Vasilis Ntziachristos, chef du centre de bio-ingénierie et directeur de l'Institut d'imagerie biologique et médicale (IBMI) à Helmholtz Munich, ainsi que professeur et directeur de la chaire d'imagerie biologique à l'université technique de Munich, a relevé ce défi en mettant au point une nouvelle méthode de microscopie appelée microscopie optoacoustique hyperspectrale dans l'infrarouge moyen (HyFOPM), qui permet de rendre les lipides visibles sans les étiqueter.
La méthode consiste à éclairer l'échantillon avec une lumière infrarouge moyenne pulsée à plusieurs longueurs d'onde distinctes, une illumination dite "hyperspectrale". Les lipides absorbent des bandes spécifiques de cette lumière, produisant une augmentation minime et brève de la température qui génère des ondes ultrasonores. Ces ondes sont détectées par des transducteurs à ultrasons et converties en une image spectrale. L'analyse informatique de cette image spectrale produit ensuite des cartes montrant la distribution des différents lipides dans l'échantillon.
"Le schéma d'absorption est caractéristique des différentes molécules et agit comme une empreinte moléculaire unique", explique Francesca Gasparin, scientifique à l'IBMI et à la TUM, et premier auteur de l'étude. "Cette empreinte dans l'infrarouge moyen nous permet de distinguer différents lipides sans avoir besoin d'étiquettes externes".
La région de l'empreinte fait la différence
Ce qui rend cette méthode unique, ce sont les longueurs d'onde qu'elle utilise. De nombreuses approches sans étiquette s'appuient sur des gammes spectrales dominées par les liaisons présentes dans une grande variété de biomolécules, produisant des signaux similaires qui rendent difficile la distinction des différentes classes de lipides.
L'équipe se concentre au contraire sur la région dite de l'empreinte digitale, où les caractéristiques d'absorption proviennent principalement de modes vibrationnels très caractéristiques de la structure moléculaire de chaque lipide. Cela signifie que la méthode peut détecter non seulement les éléments constitutifs d'une molécule, mais aussi la manière dont ils sont agencés les uns par rapport aux autres. En opérant dans cette région, la technique peut différencier les espèces lipidiques, même celles qui sont chimiquement similaires, comme les glycérophospholipides et la sphingomyéline.
Un stress minimal pour les cellules
Pour tester la fiabilité de ces empreintes chimiques, l'équipe a comparé ses mesures à la spectroscopie infrarouge classique, qui a servi de référence. Si la méthode traditionnelle permet de mesurer avec précision les composés dissous et les gouttelettes de solution, elle n'est pas adaptée aux cellules vivantes, qui nécessitent une préparation spéciale susceptible de les stresser.
La nouvelle technique de microscopie a non seulement reproduit les spectres lipidiques attendus en solution, mais elle a également permis d'effectuer des mesures directement dans des cellules vivantes. "L'un des principaux avantages de HyFOPM est que l'observation des lipides sans marquage n'entraîne qu'un stress minimal pour les cellules vivantes", explique Francesca Gasparin.
Perspectives : De la culture cellulaire aux applications proches du patient
À long terme, les chercheurs entrevoient des applications dans un large éventail de recherches sur les lipides, de la science fondamentale aux applications médicales qui ont été jusqu'à présent difficiles d'accès.
"Le fait de pouvoir suivre et cartographier les classes de lipides dans les cellules vivantes sans étiquette ouvre de nouvelles voies pour comprendre les processus pathologiques et surveiller l'activité métabolique, non seulement dans les cellules mais aussi chez l'homme", explique le professeur Vasilis Ntziachristos. "La prochaine étape consiste à accélérer la méthode et à la tester systématiquement dans des systèmes cellulaires complexes, afin d'acquérir des connaissances sur le développement des maladies et l'action des médicaments. Enfin, nous souhaitons l'utiliser chez l'homme pour la surveillance continue des métabolites, afin d'obtenir des biomarqueurs exploitables pour un large éventail de pathologies relevant du syndrome cardiométabolique et au-delà."
Note: Cet article a été traduit à l'aide d'un système informatique sans intervention humaine. LUMITOS propose ces traductions automatiques pour présenter un plus large éventail d'actualités. Comme cet article a été traduit avec traduction automatique, il est possible qu'il contienne des erreurs de vocabulaire, de syntaxe ou de grammaire. L'article original dans Anglais peut être trouvé ici.
Publication originale
Francesca Gasparin, Alexander Prebeck, Alice Soldà, Nasire Uluç, Sarah Glasl, Constantin Berger, Miguel A. Pleitez, Vasilis Ntziachristos; "Differentiation of sphingomyelin and cholesterol by hyperspectral mid-infrared detection of single-bond vibrational modes in the fingerprint region"; Nature Methods, 2026-3-30