Rosa: die Trendfarbe für niedersächsische Forscher
Sonderforschungsbereich "Roseobacter" in Niedersachsen etabliert
Anzeigen
Photosynthetisch aktive Bakterien der Roseobacter-Gruppe haben ein gemeinsames Charakteristikum: sie sind rosa-rot gefärbt. Aber nicht nur das: sie bilden eine der wichtigsten Gruppen unter den marinen Bakterien. Grund genug, sie in einem Sonderforschungsbereich (SFB) genauer unter die Lupe zu nehmen. Der SFB "Roseobacter" startete zu Jahresbeginn. Der Deutschen Sammlung von Mikroorganismen und Zellkulturen stehen DFG-Fördermittel in Höhe von 855.000 Euro zur Verfügung.
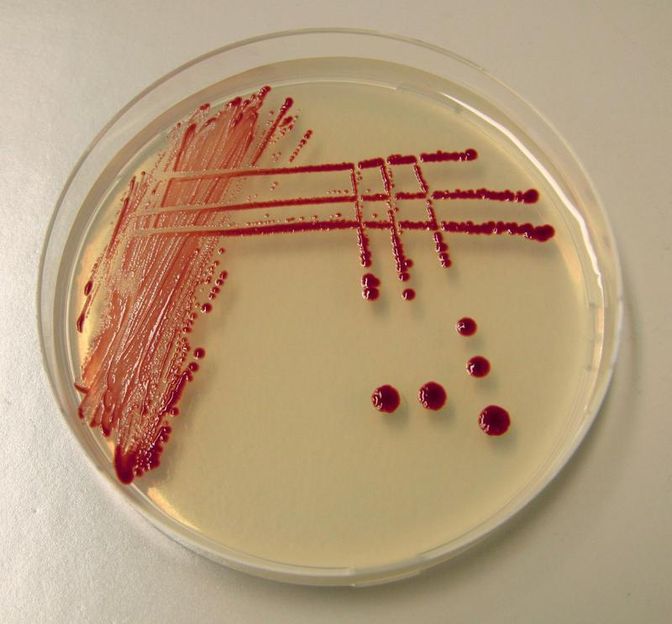
Dinoroseobacter shibae.
DSMZ/Wozniczka
"Die DSMZ kann hier ihre Stärken hier voll ausspielen", sagt PD Dr. Hans-Peter Klenk, Leiter der Abteilung Mikrobiologie an der DSMZ. Mit gleich zwei Forschungsvorhaben ist die Braunschweiger Sammlung am Langzeitprojekt beteiligt.
Projekt "Plasmide"
Die Projektleiter Dr. Silke Pradella und PD Dr. Jörn Petersen analysieren die Bedeutung und Evolution von sogenannten Plasmiden in der Roseobacter-Gruppe. Plasmide sind genetische Elemente, die zusätzlich zu normalen Bakterien-Chromosomen in der Zelle existieren und während der Zweiteilung an die Tochterzellen weitervererbt werden. Oft sind auf Plasmiden Abbauwege für schwer zugängliche Kohlenstoffquellen, Antibiotika-Resistenzen und andere nützliche Gene hinterlegt. Unter spartanischen Umweltbedingungen bieten diese Plasmide einen erheblichen Vorteil im Kampf ums Überleben. Unter Laborbedingungen werden diese Plasmide aber schnell zum unnötigen Ballast und gehen dann verloren.
An der DSMZ werden die beiden Bakterien Dinoreoseobacter shibae und Marinovum algicola untersucht. Beide Bakterien leben assoziiert mit marinen Algen, für D. shibae ist eine echte Symbiose zu beiderseitigem Nutzen nachgewiesen worden. Das Bakterium produziert Vitamin B12 für die Alge, umgekehrt versorgt die Alge das Bakterium mit Kohlenstoffverbindungen. D. shibae besitzt mindestens fünf Plasmide, M. algicola leistet sich sogar den Luxus, an jede Tochterzelle zwölf Plasmide weiterzuvererben.
Bisher erfolgte die Klassifikation von Plasmiden fast ausschließlich "nach Gefühl" - so wie man Fledermäuse, Schmetterlinge und Vögel aufgrund ihrer Flugfähigkeit in einer gemeinsamen Gruppe unterbringen könnte. "Damit muss die Forschung endlich aufräumen", sagt Jörn Petersen. An der DSMZ soll ein neues System zur Klassifizierung entwickelt werden, das auch Vorhersagen über das Vorkommen verschiedener Plasmide in einem Bakterium erlaubt. Denn nicht jedes neu hinzugewonnene Plasmid kann mit den schon vorhandenen in einer Zelle koexistieren, sie sind häufig "inkompatibel".
Viele Plasmide der Roseobacter-Gruppe sind bereits sequenziert, aber ihre Funktionen liegen noch weitgehend im Dunklen. "Es gibt Gene, die eine gewisse strukturelle Ähnlichkeit zu schon bekannten Genen haben - aber es stecken auch unzählige neue Gene in den Plasmiden.", so Silke Pradella. Die Funktion der plasmidären Gene wollen die Forscher mithilfe von bakteriellen Mutanten klären, denen sie einzelne Plasmide gezielt und dauerhaft entfernen. Dieses "Plasmid-Curing" ist methodisch anspruchsvoll, weil alle übrigen Plasmide auch unter Laborbedingungen im Bakterium erhalten bleiben müssen. Aber die Methode gibt den Forschern wichtigen Aufschluss über die plasmidären Gene: denn alle Eigenschaften, die den Mutanten dann fehlen, müssen im Plasmid gesteckt haben.
Projekt "Phylogenomik"
Die Bioinformatiker PD Dr. Markus Göker und PD Dr. Hans-Peter Klenk haben sich vorgenommen, die Genome der Roseobacter-Gruppe zu analysieren. Sie erforschen zum einen die Phylogenie die stammesgeschichtliche Entwicklung der Bakteriengenome, und arbeiten zum anderen an der funktionellen Genom-Analyse, die es erlaubt, die Umsetzung und Regulation genetischer Information in der Bakterienzelle zu betrachten.
"Wir haben die Komplettsequenzierung vieler Bakteriengenome in den letzten Jahren stark vorangetrieben.", so Klenk. "Die Roseobacter-Gruppe gehört inzwischen zu den Gruppen mit den meisten untersuchten Genomen. Das kommt uns bei unseren Arbeiten sehr entgegen."
Klenk und Göker wollen gewissermaßen den kleinsten genomischen Nenner finden. Was braucht ein Bakterium, um Mitglied dieser Gruppe zu sein? Kann man diese Information zur stammesgeschichtlichen Einordnung nutzen? Welche der vorhandenen Gene sind bei der Zweiteilung vererbt, welche sind durch sog. "horizontalen Gentransfer" von ganz anderen Bakterien erworben worden? Wie beschreibt man, wenn verschiedene Gene verschiedene Stammbäume ergeben, am besten die Evolution dieser Bakterien?
Neben dem Genom soll deshalb auch der Phänotyp - das Erscheinungsbild der Bakterien mit allen Eigenschaften - untersucht werden. Dazu nutzen die Forscher das BiOLOG-System. Im BiOLOG-System werden beispielsweise Stoffwechseleigenschaften getestet - so wird für verschiedenste Substrate überprüft, ob sie durch das Bakterium verwertet werden können. Insgesamt nimmt das System rund 2.000 Eigenschaften unter die Lupe. Die so gewonnenen physiologischen Daten sollen in Beziehung zu den genomischen Daten der Bakterienstämme gesetzt werden. Die Forscher erhoffen sich davon auch Verbesserungen in der biologischen Beschreibung von Genen - derzeit ist in Genomsequenzen ein 40%iger Anteil von Genen mit unbekannter Funktion keine Seltenheit.
Letztendlich entwickeln die Bioinformatiker ein Modell, das die Evolution der Roseobacter-Gruppe beschreibt und die taxonomische Einordnung neuer Stämme in diese Bakteriengruppe erleichtert.